Milchsäurebakterien
Schneller und spezifischer Nachweis der getränkeschädlichen
Bakterien-Gattungen Lactobacillus, Leuconostoc und Pediococcus
Artikel-Nr.: 00230014
Laboranalyse: Nachweis von getränkeschädlichen Milchsäurebakterien
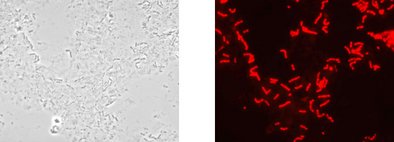
Alkoholische und nicht-alkoholische Getränke werden auf die Anwesenheit von Getränkeschädlingen der Gattungen Lactobacillus, Leuconostoc und Pediococcus untersucht.
Sie erhalten die Ergebnisse bereits am 3. Werktag nach Probeneingang. Bei fertigen Anreicherungen spätestens am 1. Werktag nach Probeneingang.
Qualitativer oder quantitativer Nachweis?
Qualitativ
Wie erfolgt die Analyse?
Durch Anwendung der zuverlässigen VIT® Gensondentechnologie.
Welche Anforderungen bestehen an die einzuschickende Probe?
Produkt- oder Rohstoffproben:
- Bier, Wein, Säfte & Softdrinks, mind. 100 ml
- Saftkonzentrate, mind. 25 ml
- Wasserproben (z.B. Mineralwasser, Spülwasser etc.), mind. 150 ml
Vorangereicherte Proben:
- Anreicherungsbouillon (10 ml) oder Agarplatte mit Kolonien: Dies führt zu einer Beschleunigung der Schnellanalytik (die Befunde werden dann schon für den 1. Werktag nach Probenerhalt erwartet).
Ideal für eine Untersuchung auf alle relevanten Getränkeschädlinge ist unser Screening "Getränkeschädlinge", speziell für Bierproben empfiehlt sich das VIT® Bier Screening.
Nutzen Sie für eine Analyse Ihrer Proben direkt vor Ort unseren Testkit VIT® Milchsäurebakterien.
Ihre Vorteile
spezifischer Nachweis von Lactobacillus, Leuconostoc und Pediococcus
nur Nachweis von vitalen Bakterien
kurze Nachweiszeit
höchste Spezifität
Untersuchung von unterschiedlichsten Probenmaterialien